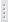Zafrin:
bioaktivní látka produkovaná mořskými bakteriemi Pseudomonas.
Jiří
Patočka
Pseudomonas je rod gramnegativních proteobakterií, které byly izolovány z půdy, ze sladkých vod i z moře. Tento rod se skládá z mnoha druhů, které jsou geneticky velice různorodé (Kersters et al., 1996). Na základě analýzy a podobnosti rRNA jsou konány pokusy o jejich roztřídění (Moore et al., 1996; Anzai, 2000), ale jich systematika je stále nedokončená, vykazuje obrovskou dynamiku a pravděpodobně dozná v budoucnosti mnohé zněny (Marín et al., 2021).

Moderní výzkum těchto mikroorganismů, zejména těch mořských ukázal, že produkují obrovské množství sekundárních metabolitů, které představují dosud nevyužitý rezervoár nových bioaktivních látek. Z bakterií bylo izolováno až dosud 3800 biologicky aktivních metabolitů. Pseudomonas produkuje 795 bioaktivních látek, včetně 610 antibiotik a 185 látek s jinými než antibiotickými vlatnostmi. Jejich systematický výzkum stále probíhá a přináší stále nové a nové látky zajímavých struktur a neméně zajímavých biologických účinků. Jednou z takových látek je také zafrin (4β-methyl-5,6,7,8-tetrahydro-1-(4β-H) -fenanthrenon) (Uzair et al., 2008).
Screeningem 100 druhů bakterií, izolovaných ze střevního traktu mořských ryb z okolí Karáčí (Pákistán), byla objevena bakterie Pseudomonas stutzeri (CMG 1030), jejíž izolát vykazoval výraznou inhibiční aktivitu proti několika patogenním bakteriím, včetně kmenů MRSA (Bushra, 2007). Chemické vyšetření ethylacetátového extraktu prokázalo, že tímto antibakteriálně účinným metabolitem je látka, která byla nazvána nazvaný zafrin (4β-methyl-5,6,7,8-tetrahydro-1-(4β-H) -fenanthrenon) (Uzair et al., 2008). Struktura zafrinu byla objasněna spektroskopickými metodami zahrnujícími 1H-nukleární magnetickou rezonanci (NMR), 13C-NMR, 1D-NMR a 2D-NMR spektroskopii.

Jedním z velkých problémů, se kterými se zdravotní péče v současné době potýká, je vznik bakterií rezistentních vůči antibiotikům a zejména šíření kmenů patogenních bakterií Staphylococcus aureus (MRSA) rezistentních na methicilin. Skupina MRSA je nyní odolná téměř proti všem běžně používaným antibiotikům a dokonce se objevila rezistence na jedno z antibiotik "poslední volby", vankomycin (Courvalin, 2006; Deurenberg et al., 2007). To byl jeden z důvodů, proč byl realizován screeningový program produkce antibakteriálních látek mořskými bakteriemi. Výsledkem tohoto výzkumu byl objev zafrinu. Zdaleka to však nebyl objev první, ani poslední. Mořské pseudomonády představují bohatý zdroj nových molekul a jsou potenciálním dosud nevyužitým zdrojem medicinálně relevantních bioaktivních látek (Isnansetyo a Kamei, 2009).
Zafrin v experimentech in vitro vykazoval silnou antibakteriální aktivitu jak proti grampozitivním, tak proti gramnegativním bakteriím. Purifikovaný roztok zafrinu byl účinný proti několika lidským patogenům, včetně Staphylococcus aureus a Salmonella typhi. Naproti tomu zafrin neinhiboval růst eukaryotických organismů Candida albicans a Schizosaccharomyces pombe. Minimální inhibiční koncentrace (MIC) pro gram-pozitivní bakterie se pohybovala v rozmezí od 50 do 75 μg/ml a pro gram-negativní bakterie v rozmezí od 75 do 125 μg/ml. Zafrin lýzoval buňky Bacillus subtilis pěstované v osmoticky chráněném médiu. Další vyšetření pomocí B. subtilis ukázalo, že sloučenina narušuje cytoplazmatické membrány, protože molekula je amfifilní (Uzair et al., 2008).
Literatura
Anzai Y, Kim H, Park J-Y, Wakabayashi H, Oyaizu H. Phylogenetic affiliation of the pseudomonads based on 16S rRNA sequence. Int J Syst Evol Microbiol 2000; 50: 1563–1589.
Bushra U. Genetic diversity among bacterial flora of Baluchistan coast. (Doctoral dissertation, University of Karachi) 2007.
Courvalin P. Vancomycin resistance in gram-positive cocci. Clin Infect Dis. 2006; 42 Suppl 1: S25-S34.
Deurenberg RH, Vink C, Kalenic S, Friedrich AW, Bruggeman CA, Stobberingh EE. The molecular evolution of methicillin-resistant Staphylococcus aureus. Clin Microbiol Infect. 2007; 13(3): 222-235.
Isnansetyo A, Kamei Y. Bioactive substances produced by marine isolates of Pseudomonas. J Ind Microbiol Biotechnol. 2009; 36(10): 1239-1248.
Kersters K, Ludwig W, Vancanneyt M, De Vos P, Gillis M, Schleifer KH. Recent changes in the classification of pseudomonads: an overview. Syst Appl Microbiol 1996; 19: 465–477.
Marín O, González B, Poupin MJ. From Microbial Dynamics to Functionality in the Rhizosphere: A Systematic Review of the Opportunities With Synthetic Microbial Communities. Front Plant Sci. 2021;12: 650609.
doi:10.3389/fpls.2021.650609Moore ERB, Mau M, Arnscheidt A, Böttger EC, Hutson RA, Collins MD, van de Peer Y, de Wachter R, Timmis KT. The determination and comparison of the 16S rDNA gene sequence of species of the genus Pseudomonas (sensu stricto) and estimation of the natural generic relationships. Syst Appl Microbiol 1996; 19: 478–492.
Uzair B, Ahmed N, Ahmad VU, Mohammad FV, Edwards DH. The isolation, purification and biological activity of a novel antibacterial compound produced by Pseudomonas stutzeri. FEMS Microbiol Lett. 2008; 279(2): 243-250.